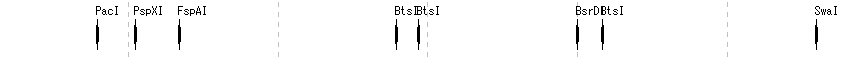機能と操作
インシリコバイオロジー社のソフトウェアを使用して実現できる先進的かつユニークなソリューションを多数掲載しています。このソリューション記述においては製品を特定しません。どのような課題に対して、主としてインシリコバイオロジー社の製品がどのような解決方法を提供できるかを述べています。したがって、あるソリューションについては、1つの製品ではなく、外部ソフトウェアあるいは手作業を含めた総合的な解決方法を記述しています。
サブカテゴリ
- IMCはゲノム時代の新しい概念による配列解析ソフトウェアです。
- 分子生物学のセントラルドグマに沿った操作を実現しています。
- ゲノム塩基配列を基本として、様々な解析を実行することが可能です
- IMCは、「まずゲノム塩基配列ありき」のトップダウンアプローチに基づく新しい時代のソフトウェアです。
- 利用者毎の独自のカスタマイズ機能が豊富です。
- 分子生物学実験の補助やシミュレーションに使用できます。
- 研究用だけでなく、分子生物学の教育・学習用のソフトウェアとしても充分利用できます。
- インシリコのクローニング実験が可能です。
- 目に見えない分子生物学実験を理解する助けになります。
- 独自開発のため、研究者の要望を迅速に反映し、頻繁な改良や機能追加を実現しています。
- 研究者や学生が日常的に利用しているWindowsやMac上で動作します。
|
- インストール方法
- ライセンスの取得と更新
- 起動方法
- 終了方法
- 最新Versionの確認とダウンロード
- 配列ファイルの読込と保存
- フィーチャーマップの基本操作
- ヘルプのダウンロード
- ヘルプの操作
- ウェブからの情報収集
- フォーラムの利用
|
 |
- Windowの構成
- メインウィンドウ各部の名称と機能
- ルートディレクトの作成と切替
- ディレクトリーツリーによる配列ファイルの階層管理
- 配列ロードディレクトリの操作
- 参照ロードディレクトリの操作
- ウィンドウの操作
- 画面キャプチャー
- フィーチャーレイアウトスタイルの切替
- メニューバーの操作
- ボタンツールボックスの操作
- フィーチャーとフィーチャーキー
- フィーチャーマップの操作
- 参照マップの操作
- インポート・エキスポート
- 読込と保存
|
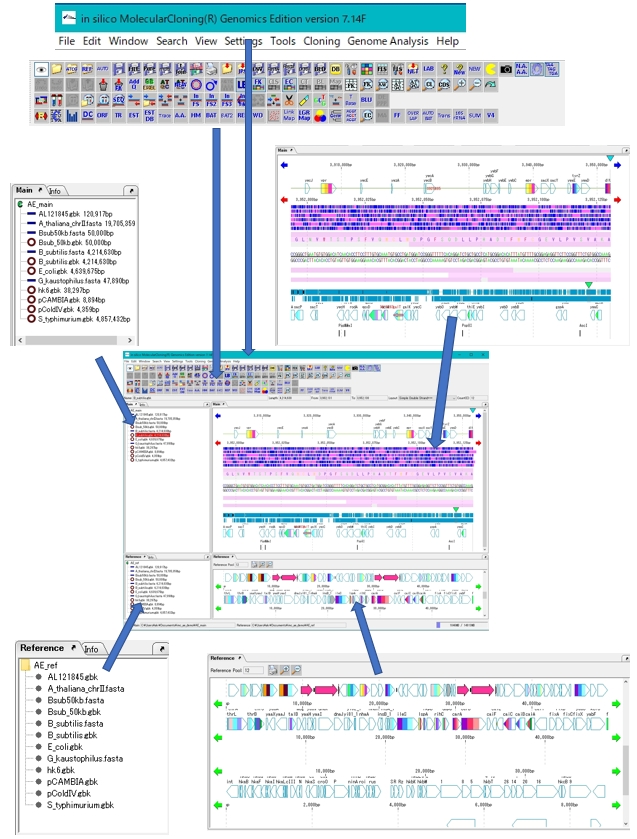 |
IMCのワークベンチは以下の要素から構成されます。
- ヘッダー領域
- メニューバー
- ツールボックス*
- 上部インディケーター領域
- メインディレクトリーツリー*
- 参照ディレクトリーツリー*
- メインフィーチャーマップ*
- 参照フィーチャーマップ*
- 下部インディケーター領域
*印の要素は、ワークベンチウィンドウからのドックアウト(取り外し)、ドックイン(組み入れ)が可能です。
|
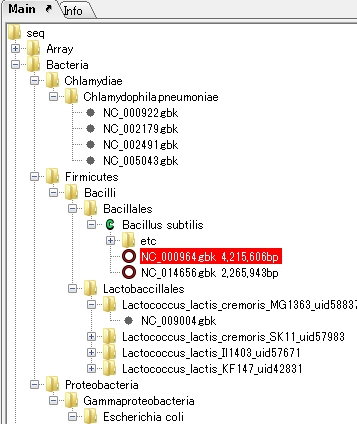 |
- 従来、保存した配列が行方不明となりがちだった欠点を改善。
- ロードされた配列がディレクトリツリー形式で管理されます。
- rootノード以下に複数の配列フォルダーを登録できます。
- カレント配列ロードフォルダー上の配列全部がメモリー上にロードされるため、ノード切換が高速に実行できます。
- ロード配列のコピーが生成され、更新もコピーに対して実行。
|
既定フィーチャーキー
フィーチャーキーの登録、編集、削除
テンプレート機能
フィーチャーキー検索
IMCが独自に設定しているフィーチャーキーを説明します。
これらのフィーチャーキーを一括取り除く機能もあります。
Qualifierの種類と役割について説明します。
GenBank / EMBL / DDBJの国際塩基配列データベースの規約において、Qualifierの使用規則が定められていますが、IMCでは独自のQualifierをも追加して、有用な機能を実現しています。IMCが独自のQualfierを設定している理由は、GenBank / EMBL ファイルに直接制御データを記述し、利用者が配列ファイルの取り扱いが簡単になるためです。
上記規約で取り決められたQualifier
IMCが独自に追加したQualifier
/genomemap=
/new=
/update=
Featureの属性を示すQualifierの表示方法や編集方法に関する情報を提供しています。
以下はFeatureに記述されているQualfierの値の表示方法を2つを表しています。
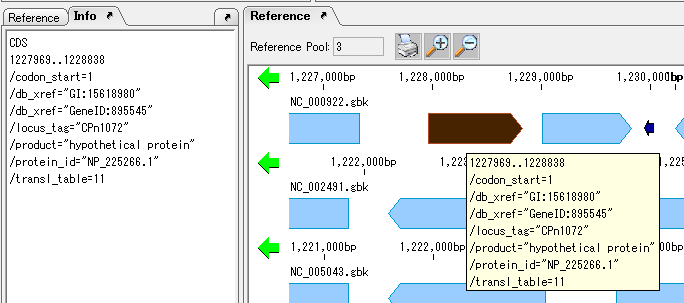
ゲノム配列上におけるフィーチャーの位置にかんする説明。
制限酵素やPCR増幅によるフィーチャーの断片化について説明します。
PCRやライゲーションによるフィーチャーの合成を説明します。
フィーチャーフュージョン機能は、2つの同一positionにある同一Feature Keyに属するフィーチャーを1つに融合する機能です。融合されるそれぞれのフィーチャーに記録されていたQualifierは融合されたフィーチャーのQualifierとしてどちら側のQualifierも同等に保持されます。
この機能により、同一のフィーチャーに対して別々に付けられた複数のアノテーションを簡単に1つにまとめることができます。
フィーチャー演算子は、同一Feature Keyに属する2つの互いにオーバーラップするフィーチャーの論理演算を行い、新たなフィーチャーを生成する機能です。
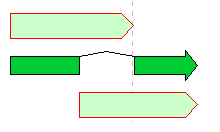 上下がオーバーラップするフィーチャーで、中央が演算生成されたフィーチャー。
上下がオーバーラップするフィーチャーで、中央が演算生成されたフィーチャー。
個々のフィーチャーにリンクし、その可視化ツールを起動できるのは以下のものがあります。
分子立体構造ファイルとその可視化ツール、
文献ファイル(pdf)とPDF表示ツール
フィーチャーに連番を付加することができます。
具体的には、連番を付加する対象のフィーチャーのQualifierの一つに連番を付ける編集操作になります。
対象となるフィーチャーや連番を付けるQualifierはある程度自由に選択できます。
複数の配列ファイルにまたがって連番をつける機能もあります。
また、検索の結果絞り込まれたフィーチャーに連番を付加することも可能です。
IMC の フィーチャーマップ は多様なカスタマイズ機能(フィーチャーレイアウトスタイル対応)を有しており、望み通りの遺伝子地図などを描画、印刷することができます。
遺伝子地図 (フィーチャーマップ)作成、地図のカスタマイズ(フィーチャー配置方法、形状、カラー、ラベル)
独自フィーチャーキーの登録
環状DNA 対応のスクロール、地図描画
高速ズーム、スクロール、ナビゲーションレーン
GenBank/EMBL フォーマットファイルとの連動
コンテントマップ(組成ファイル)のグラフ描画・印刷
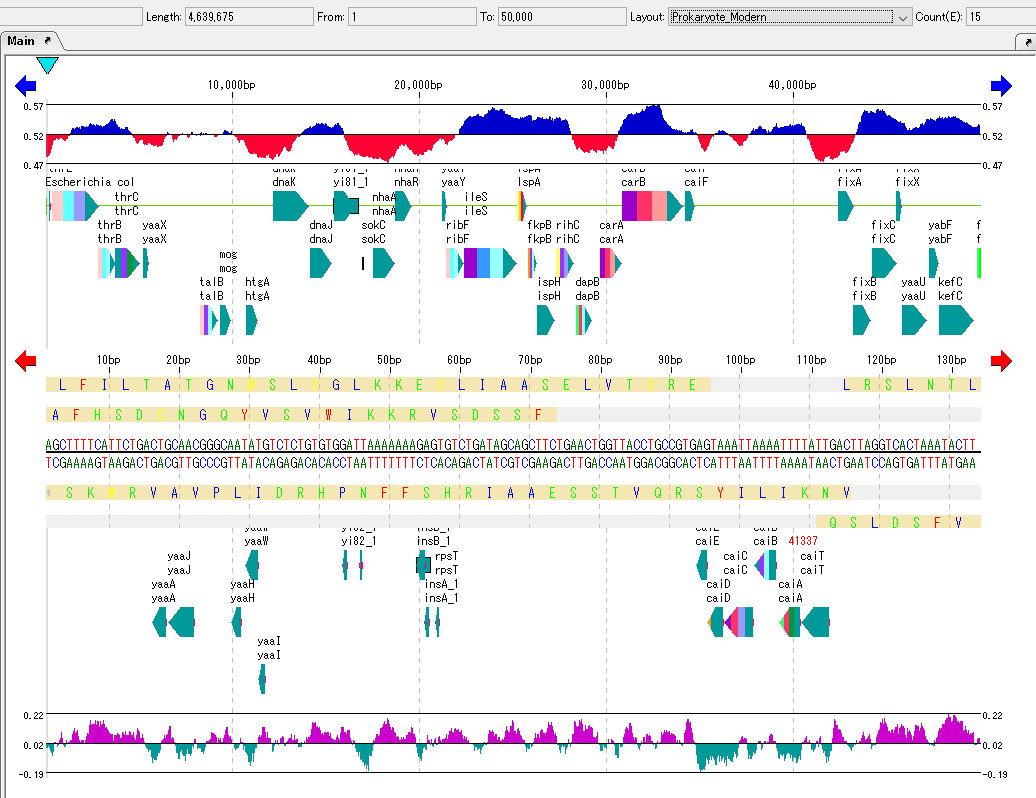
フィーチャーレイアウトスタイルを使用することにより、複数の機能別レーンを組み合わせてフィーチャーマップを描画する際に予め登録したレイアウトを適用することにより、簡単に複雑なフィーチャーレイアウトをもつフィーチャーマップを描画することができます。
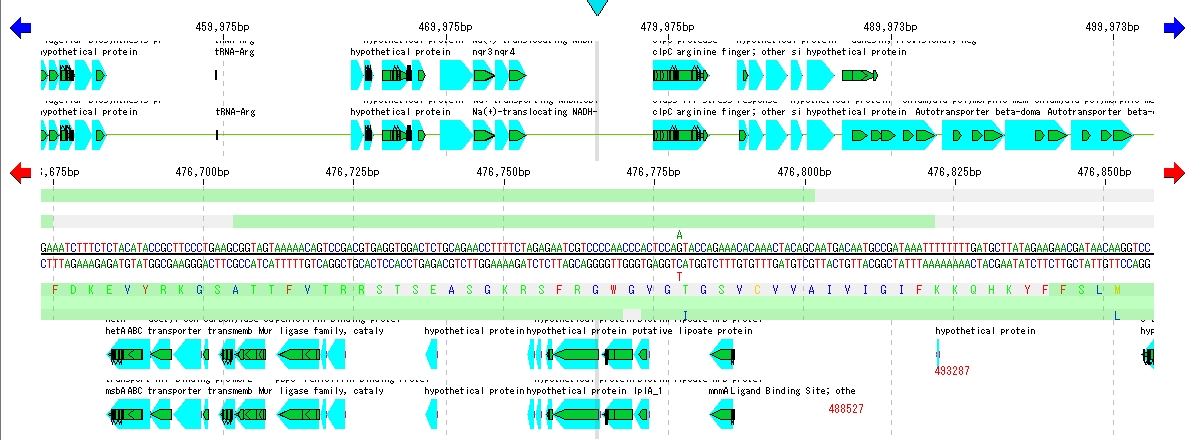
配列レーンには、現在ロードされている塩基配列ファイルの塩基および、もしそこがコーディング領域である場合はアミノ酸配列がそれぞれストランド別に表示されます。
配列レーンはフィーチャーマップのどの位置にも配置することができます。必要であれば2個以上の配列レーンを1つのフィーチャーマップ上に配置できます。
塩基4種類とアミノ酸20種類はそれぞれ個別に異なるカラーで表示することができます。
描画カラーおよびフォントサイズの変更は、フィーチャーセッティングのSequence Lane タブペインで行います。
アミノ酸1文字コードをコドンのどの位置に置くかを変更することができます。
スタートコドン候補やストップコドンの位置を示す矩形をフレーム表示領域に表示できます。
フォントタイプの変更はできません。

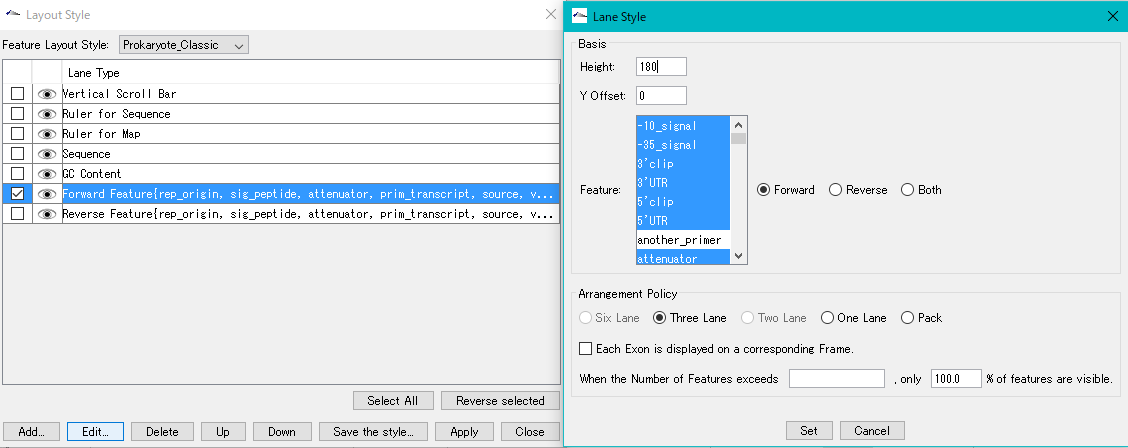
- 上図は、Forward StrandにあるCDS、rRNA、tRNAを3フレーム表示にした フィーチャーレーン のサンプルです。
- フィーチャーレーン設定ダイアログ からは以下の機能が実行できます。
- 表示フィーチャーキー(複数)選択、ストランド選択、配置方法(Six Lane, Three Lane, Two Lane, One Lane, Pack)、表示鎖変更(Forward, Reverse, Both)、エクソン 表示方法変更、配置密度、レーンの高さ変更、オフセット 変更。

- コンテント・プロファイルレーン設定ダイアログから設定可能な項目は以下の通りです。
- レーン高さ変更、表示コンテント選択(GC Contentなど6コンテント、GC/AT Skew, Cumulative GC/AT Skew, Import Map Data, Fickett Profile)、背景色変更、プロファイルグラフのパラメータ変更、スライディングウィンドウパラメータ変更、間引き機能、グラフカラー変更。
Navigation Laneは、Feature Map全体の鳥瞰地図を表示し、スライダでFeature Mapの表示位置を移動することができます。

- ナビゲーションレーン設定ダイアログから変更可能な項目は以下の通りです。
- 表示対象フィーチャー(複数)選択可能。ストランド選択(Forward, Reverser, Both)、配置方法選択(Six Lane, Three Lane, Two Lane, One Lane, Pack)、間引き設定変更。
- 制限酵素レーン設定ダイアログから変更可能な項目は以下の通りです。
- レーン高さ、セット切替、制限酵素リストの絞り込み(認識配列長、パリンドローム性、末端形状(Blunt, Sticky)、DAM/DCM、対象配列の切断箇所数、制限酵素の選択。
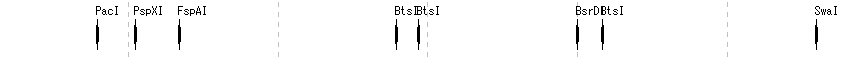
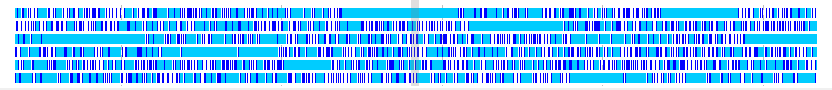
- Frame Laneは6個のフレーム別にストップコドンが連続して出現しない領域を表示するレーンです。
- 6個のフレーム毎にストップコドンからストップコドンまでが指定コドン数以上ある領域を示します。
- ストップコドンの存在しない領域を右クリックして、新規フィーチャーとして登録できます。
発現プロファイルレーンは、遺伝子発現プロファイルを表示するレーンです。(アレイエディション以上に実装)
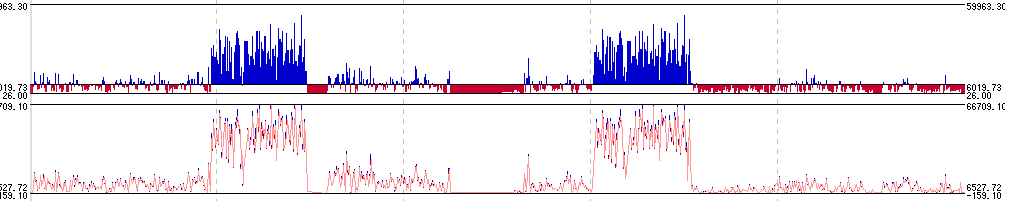
縦スクロールバーレーン

配列スケールレーンとマップスケールレーン

IMCで使用する配列データ・ファイル、フィーチャーデータ・ファイル、オプションデータ・ファイルなどについての操作説明です。
ゲノム配列やアミノ酸配列ファイルをIMCにロードします。
外部からデータをインポートし、配列上にマッピングします。
配列からデータを抽出し、外部にエキスポートします。
制限酵素データ・ファイル、プライマーデータ・ファイル、オプションデータ・ファイルなどの操作を記述します。
| |
- 配列パターン検索(核酸・アミノ酸)、遺伝子間領域探索
- キーワード検索
- フィーチャーキー検索
- 相同性検索
- すべてのフィーチャーの塩基配列・アミノ酸配列からデータベースへの検索
- 検索用データベースの簡単作成
- 複数ゲノム配列を同時に検索可能
|
- メインカレント配列に登録されているフィーチャーキー数をカウントしリストを表示します。
- 検索対象のフィーチャーを複数選択可能で、検索範囲を限定可能です。
- 検索結果画面ではフィーチャーキー別の個数・配列上の位置・塩基長・遺伝子名・塩基配列・デスクリプションへのボタン・アノテーションへのボタンがリストされます。
- CDSではアミノ酸配列、+鎖ー鎖のみの選択、一括削除、コドン表、連番付加、FusionPCR、などの操作が可能です。
- 行をクリックすると、メインフィーチャーマップはそのフィーチャーの位置を表示します。
- CSV/FastA/GenBankフォーマットでのファイル出力が可能です。
- キーワードを入力して注釈を検索する機能です。対象フィーチャーキーを複数選択可能です。
- キーワードは複数指定可能でキーワード間の論理演算はAND/OR/NOTの選択が可能です。
- 検索範囲をCDS領域、Inter Genic領域の別に限定可能です。検索結果画面ではフィーチャーキー別の個数・配列上の位置・塩基長・遺伝子名・塩基配列・デスクリプションへのボタン・アノテーションへのボタンがリストされます.
- CDSではアミノ酸配列の週出、+鎖ー鎖のみの表示選択、一括削除、コドン表の表示、検索されてフィーチャーへの連番付加、FusionPCR機能へのリスト転送、などの操作が可能です。
- 結果リストの行をクリックするとメインフィーチャーマップはそのフィーチャ―位置のマップを表示します。
- CSV/FastA/GenBankフォーマットでのファイル出力ができます。
- Qualifier一括削除も実装されています。
- 登録されている配列パターンを複数選択して、カレント配列中に存在するパターンを検出します。
- 検索時にパターンを新規入力して検索することも可能です。検索範囲指定可能で、検索対象ストランド,も指定できます。
- 1~2文字のミスマッチ検出可能。CDS領域あるいは遺伝子間領域の探索領域も指定可能です。
- CDSの上流・下流指定領域のみの検索可能です。また、複数配列を検索対象として設定可能です。
検索結果画面では、パターン毎に検出個数、配列上の位置、上流下流の遺伝子を表示可能です。
- また、結果を新規フィーチャーとして自動登録が可能です。
- CSV/FastA形式で結果をファイル出力が可能です。
- 検索結果リストの行をクリックすると、メインフィーチャーマップはそのパターンの位置がマップの中央となるように移動し、配列レーン上の該当するパターン配列がハイライトされます。
- 遺伝子機能コード(コードは任意ですがCOG分類が一般的です)を複数選択して、それらの機能を持つCDSフィーチャーを検索します。
- 検索範囲指定可能で、複数配列を検索対象にできます。
- 検索結果画面からはそれぞれの機能分類毎のCDS数、配列上の位置、ストランド、COGの説明、locus_tag、上流下流の遺伝子、CDSの塩基配列、デスクリプションウィンドウおよびアノテーションウィンドウへのリンクが表示されます。
- アミノ酸配列を別途出力可能です。
- ヒットCDSの一括削除、Fusion PCR, コドン使用頻度表表示が可能です。
- 結果リストの行をクリックするとメインフィーチャーマップはその位置を表示します。
- CSV/FastA/GenBank形式でのリスト出力も可能です。
- 検索されたフィーチャ―だけをカレントマップ上に表示するオプションもあります。
参照ゲノムマップにゲノム塩基配列をロードするだけでBlast検索用データベースが自動的に作成され、そのデータベースに対する相同性(Blast)検索を簡単に実行できます。
相同性検索にはクエリー配列と配列データベースおよび検索プログラムの指定が必要です。
検索を実行するには以下の方法があります。
- クエリー配列を直接入力する
- クエリー配列をペーストする
- ファイルとして保存されているクエリー配列ファイルを参照する
- メインフィーチャーレーン上の1つのフィーチャーを右クリックして、そのフィーチャ―の配列をクエリー配列とする
- 参照フィーチャーマップ上の1つのフィーチャーを右クリックして、そのフィーチャ―の配列をクエリー配列とする
- メインフィーチャーレーンの選択領域(マウスドラッグで選択できます)にあるすべてのフィーチャーの配列をクエリー配列(複数クエリー)とする:GE以上に実装
検索用のデータベースには以下があります。
- カレント参照フィーチャーマップにロードされているゲノム塩基配列(CDS上のアミノ酸配列を含む)
- 登録されているゲノム塩基データベースあるいはアミノ酸配列データベース
- インターネット経由でNCBIの塩基配列データベースあるいはアミノ酸配列データベース
検索プログラムは以下から選択できます。
- BlastN
- BlastP
- BlastX
- tBlastN
- tBlastX
指定されたゲノム領域に存在するフィーチャー全部をクエリー配列として一括大量にホモロジー検索を行います。
 |
IMCには以下のように種々の表示用ウィンドウがあります。
- GenBank/EMBLビューア
- 配列ビューア
- アノテーションウィンドウ
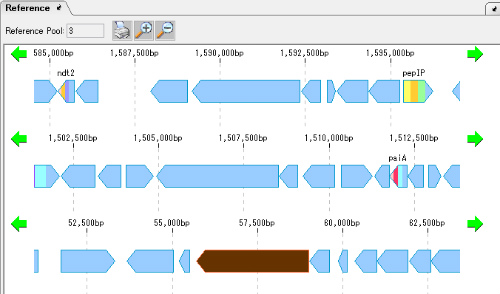
- 多重ゲノム並置ビューア(参照マップ)
- 環状ゲノムビューア・エディター
- プラスミドマップビューア・エディター
- トレースビューア・エディター
- 系統樹ビューア
- アライメントビューア
- 表示ラベルとカラー設定
|
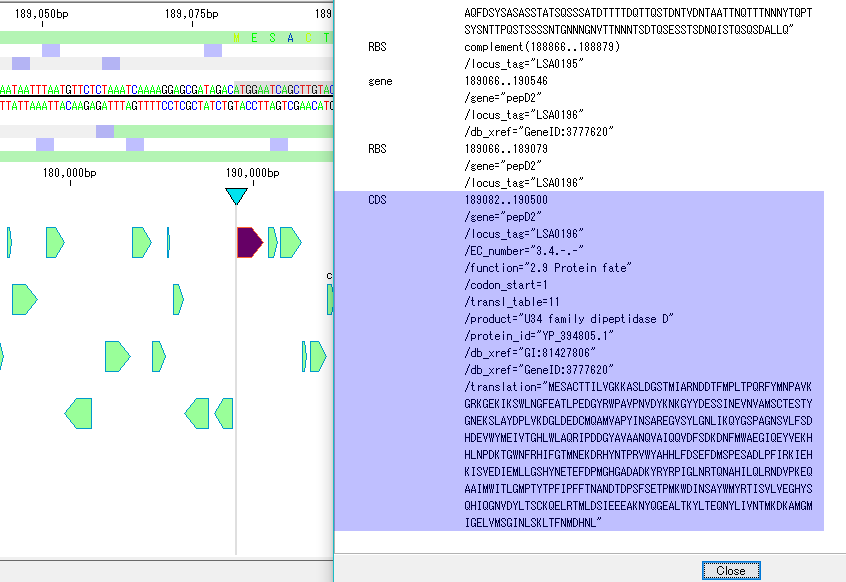
- 現在ロードされている配列ファイルをそのままの形式で閲覧できるビューアです。
- 配列や注釈をクリックすると、メインフィーチャーマップはその位置の地図を表示します。
- 逆に、このビューアを開いたまま、メインフィーチャーマップの一部をクリックすると、ファイルの対応する位置のテキストを表示できます。
- メインフィーチャーマップに現在表示されている領域の配列を表示するビューアです。
- ビューア上で表示範囲の変更、逆ストランドの表示・非表示、アミノ酸翻訳の表示・非表示、目盛りの表示方法の変更、1行の表示塩基数を表示できます。
- PDF, PNG, EMFのフォーマットでそれぞれ画像ファイルが出力できます。
- ゲノムアノテーション用に用意されたツールです。
- 主としてCDSに注釈を付加するために使用します。
- ウィンドウは3部分に分かれ、注釈を入力・直接編集できるデスクリプションペイン、相同性検索の結果をCDSフィーチャー自体にリンクさせそれらを表示し、転記できます。
- 配列表示領域には同時に既存をフィーチャーも選択的に表示できます。
- 配列、フィーチャー、目盛りの表示設定は変更できます。
- 表示内容はPDF,PNG,EMF形式で画像ファイル出力可能です。
- このウィンドウからこのフィーチャーをクエリーとする相同性検索も実行でき、結果はただちにリンクされます。
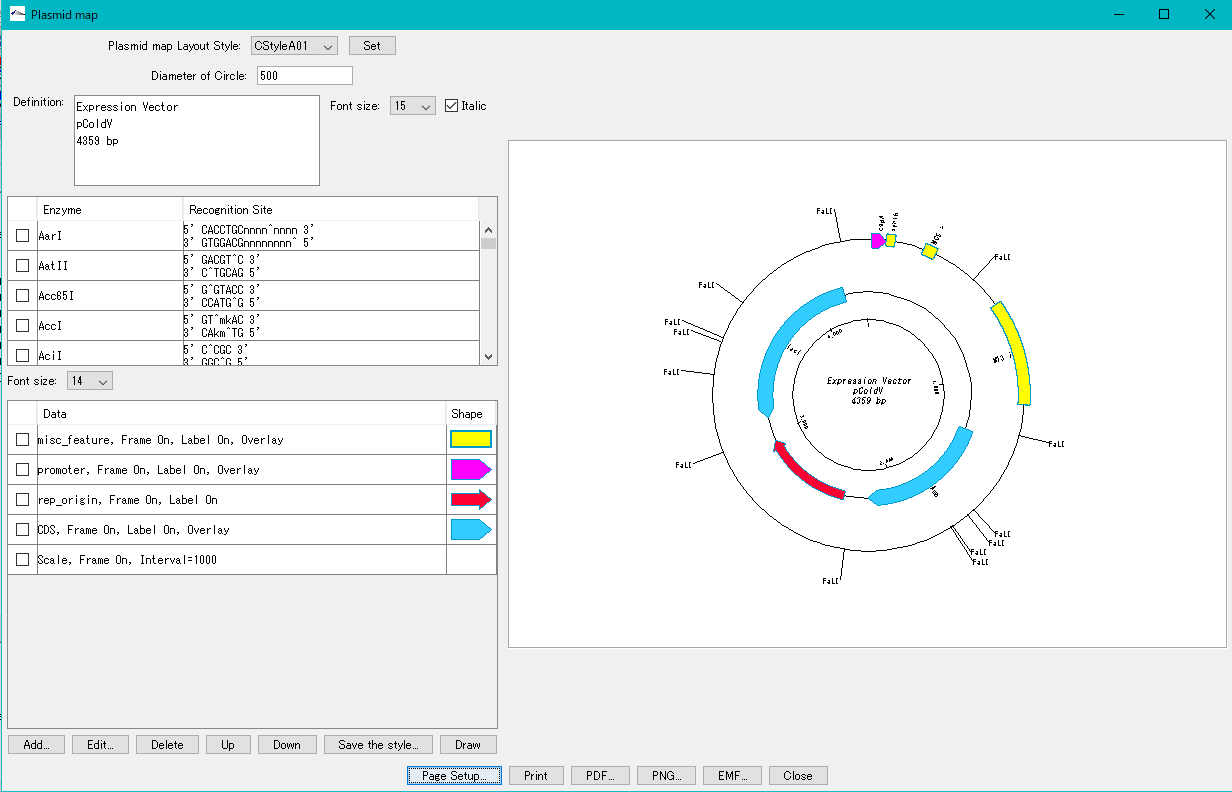
- 現在ロードされているゲノム配列に関する環状ゲノムマップの設計編集、フィーチャー同心円の追加・編集・削除、プロファイル同心円の追加・編集・削除、複数ゲノムの自動マップ生成、印刷・画像ファイル出力(PDF, PNG, EMF)が可能です。
- 設計されたサーキュラーレイアウトは、レイアウトスタイルとして保存でき、別のゲノム配列も同様のデザインで作成できます。
- 様々なスタイルの同心円をマップに追加できます。
- 1個の同心円には、複数のフィーチャーを表示設定でき、ストランド指定、カラー分類、指定フィーチャーのみの表示などができます。
- またGC含量などのコンテントマップも解像度などを自由に設定できます。
- カレントディレクトリにロードされているゲノム配列を順次切り替えて描画することも可能です。
- マップの解像度、直径、フォンサイズ、およびマップ名を変更できます。
- 環状ゲノムマップエディターに類似していますが、比較的小さな環状ゲノムを描画します。
- 環状レーンは同心円状に配置され、1つの同心円上に複数のフィーチャーキーを配置できます。
- ストランド、フレーム別、フィーチャー形状、塗りと枠のカラー指定、枠の太さ、カラー分類法の選択、ラベルの表示・非表示、ラベルとして使用するQualifierの選択、フォントサイズ、2つの同心円のオーバーレイ機能、目盛り間隔を変更できます。
- 設計したスタイルは保存でき、他のプラスミドに適用できます。
- 同心円の順序変更や追加・削除、編集が可能です。
- プラスミドマップはPDF, PNG, EMFの3種の画像フォーマットでファイル出力可能です。
- ABI, SCFのキャピラリーシーケンサからの出力ファイルを読み込んだ時に使用されるビューア・エディターです。
- 塩基配列だけでなく、その波形(トレース)を表示できます。
- ベースコールを変更できます。
デスクリプションウィンドウは、フィーチャーのQualifierに値を入力・編集するためのウィンドウです。
フィーチャー上の右クリックで起動され、そのフィーチャーのQualifierをすべて編集することができます。
また、フィーチャーのPositionも変更できます。
さらに、フィーチャーが属するFeature Keyも変更可能です。
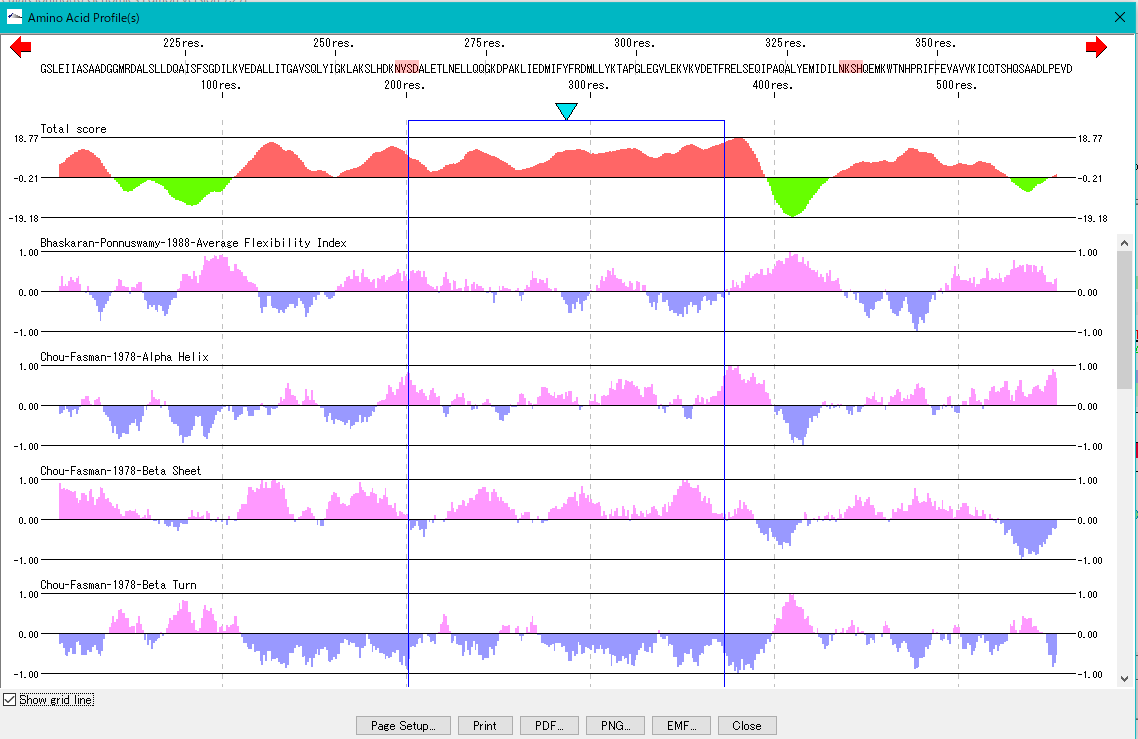
アミノ酸配列の二次構造などのプロファイルを並列表示するビューアです。個別のプロファイル表示の他に、トータルプロファイルの設計と表示、モティーフの表示などが可能です。
IMCは、クローニング実験の操作をコンピュータ上で実行できることに特徴があります。この際、特殊なデータは不要で、GenBankやEMBLなどの公的なデータベースから入手できる塩基配列データをそのままクローニングすることが可能です。クローニングは注釈付の配列をそのまま、制限酵素消化、PCRプライマー設計、PCR増幅、ライゲーションを実行できます。結果として得られるクローニング生産物はすべてGenBank/EMBLフォーマットで出力されます。Primer情報は塩基配列上に貼り付けられ保存されるるため、Primerの管理にも有用です。
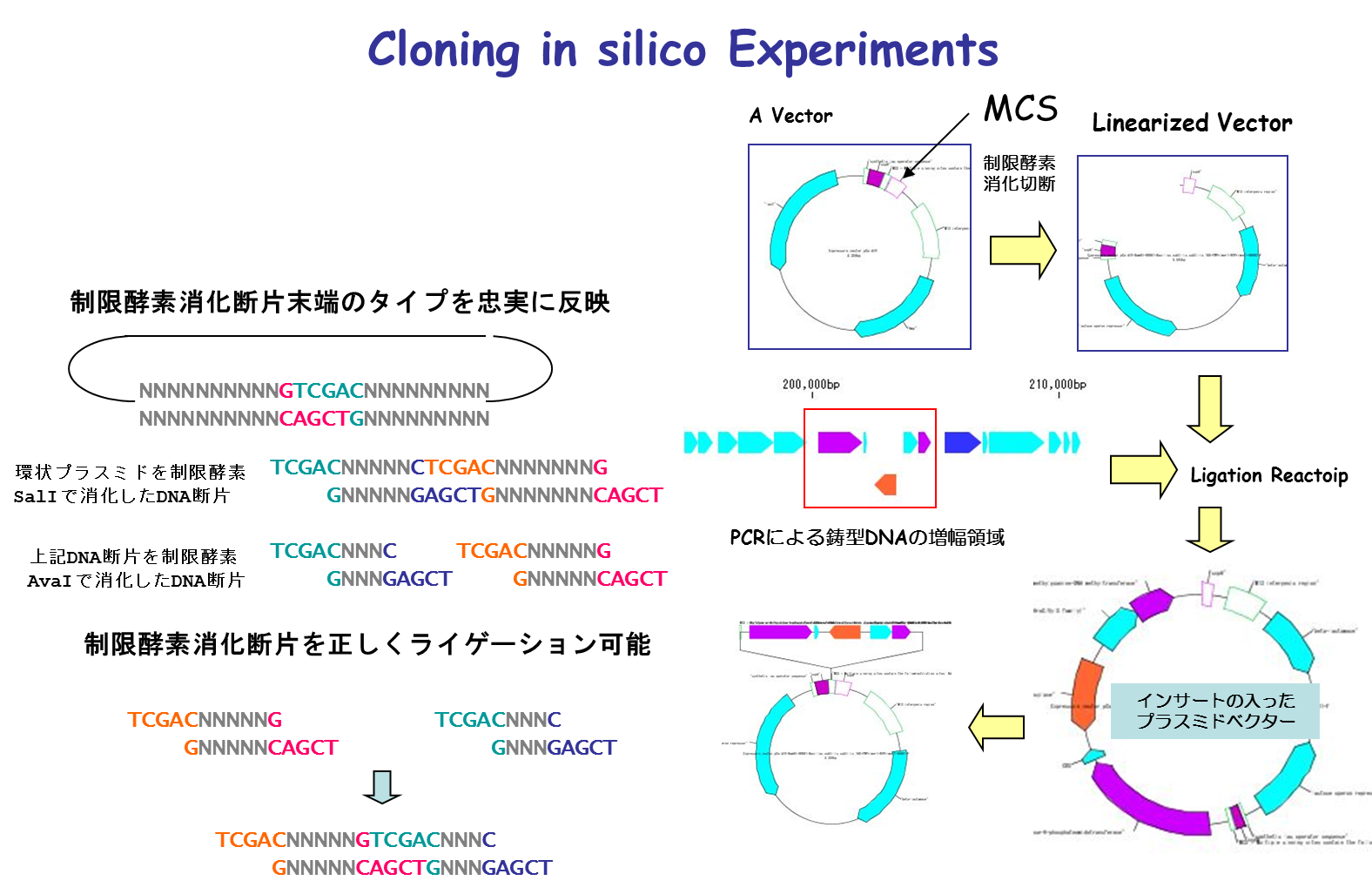
- 実際に切断・ライゲーションできるクローニング機能です。
- インシリコのクローニング実験が可能です。
- 目に見えない分子生物学実験を理解する助けになります。 分子生物学実験の補助やシミュレーションに使用できます。
- 任意のVector/Plasmidをコンストラクトできます。
- Vectorへのインサートチェックに最適な制限酵素をリストアップし、そのゲル電気泳動結果をシミュレート表示します。
- 制限酵素処理(制限酵素地図、制限酵素消化断片生成、インサートチェックに最適な制限酵素候補リスト、その他)
- PCRプライマー設計、
- 特定のフィーチャー上を避けるプライマー設計、
- PCRによる複製(注釈含む)、
- 全遺伝子を増幅する一括プライマー設計、
- プライマー管理 ライゲーション、セルフライゲーション、
- 塩基断片末端形状適合性チェック
- プラスミドマップ作成(インサート領域吹出機能) (レイアウトスタイル対応)
- 注釈を記述したままのクローニング DNA末端への制限酵素認識部位の付加
- DNA末端平滑化(Blunting)、リン酸化(脱リン酸化
- 注釈付き塩基配列の任意領域切り出し
制限酵素の管理
- 制限酵素の管理機能として、以下があります。
- 部分セット選択、
- 種類による絞り込み
- 認識塩基数の区別
- パリンドローム性
- 平滑・突出末端の区別
- DAM/DCMの有無
- 切断箇所数による違い
- 制限酵素リストの別名保存、リスト編集が可能です。
- 酵素新規登録、酵素編集、酵素削除、もできます。
制限酵素認識部位の探索機能
- 制限酵素認識部位の探索機能としては、以下があります。
- 探索領域選択、
- 認識部位検索、
- 認識部位リスト表示、
- 制限酵素地図表示、
- 複数配列からの一括検索
IMCには種々のPCR Primer設計方法があります。
単純に 配列レーン 上の塩基配列や フィーチャーレーン の領域をドラッグした範囲を プライマー として登録する機能
- 配列レーン 上からのプライマー登録
- フィーチャーレーン 上からのプライマー登録
フィーチャーレーン 上のフィーチャーや選択領域の内外を増幅するプライマーを設計する機能
- フィーチャーレーン の選択したフィーチャーを含むあるい含まれる プロダクト を増幅するための プライマー設計
- フィーチャーレーンの選択したゲノム領域を含むあるいは含まれるプロダクトを増幅するためのプライマー設計
一度に多数の領域を増幅するプライマーを一括して設計する機能(Iterate Design 機能つき:設計できなくなる領域がなくなるまで設計を繰り返す機能です)
- Batch PCR Primer Design ゲノム上の指定した フィーチャーキー をもつ全フィーチャーをすべて増幅するための バッチPCRプライマー設計
- Whole Genome Covering PCR Primer Design 全ゲノムあるいは大きなゲノム領域を PCRプロダクト が重なりを持って完全にカバーする PCRプライマー設計
- Sequencing Primer Design キャピラリーシーケンサ のワンリードでカバーできないDNA断片を シーケンシング するためのPCRプライマー設計
参考
以下は、遺伝子クラスター設計 など複数のDNA断片を一度に クローニング するためのPrimer群を一括設計する機能です。デザインからクローニングまでを実行し、クローニングされた生成物をIMCにロードできます。
- In-Fusion Design Ver.1 : In-Fusion Cloning 用のPrimer設計機能
- In-Fusion Design & Build Ver.2 : In-Fusion Cloning 用のPrimer設計機能
- In-Fusion Design & Build Ver.3 : ベクター配列にインサートするDNA断片をドロップして遺伝子クラスターを設計し、ビルドする機能
- Batch Gene Cluster Design & Build : クラスターを構成する遺伝子セットを置き換えて一括多数の遺伝子クラスターを設計し、ビルドする機能
- Combinatorial Design & Build : 遺伝子クラスター を構成する断片を コンビナトリアル に組合せ設計し、ビルドする機能
目的と概要
- ライゲーションは、分子クローニングを実行するために不可欠な実験です。IMCでは、注釈付塩基配列を含む様々な塩基配列同士を実際のクローニング実験と同様に結合して、その産物を生成します。すべての注釈はライゲーション産物にも正しく継承され、かつその産物も元の塩基配列と同様にIMCの多くの機能を使って解析することができます。
機能
- 塩基配列同士をその末端形状が相補的に一致する場合は、ライゲートし、1つの塩基配列にします。
- 最大5断片までの塩基配列をライゲーションできます。
- 3断片以上のライゲーションは、IMCGE以上で実行できます。
- 生成可能な全ライゲーション配列を生成できます。
- Version 7.24以降では、ライゲーション産物の完全相補配列を別な生成物としてカウントしています。
- GenBankやEMBL形式の注釈付塩基配列も同様にライゲーションが可能で、それらの注釈はライゲーション生成物に正しく継承されます。
- 塩基配列の末端同士の形状と配列が相補的に一致する場合は、環状塩基配列を生成します。
- 生成されたライゲーション産物における各断片のインサート方向をチェックするために使用できる制限酵素のリストを表示します。
- またそれらの制限酵素を使用した場合のゲル電気泳動パターンを表示します。
- カレントフォルダーにロードされているすべての塩基塩基配列の末端形状を表示します。
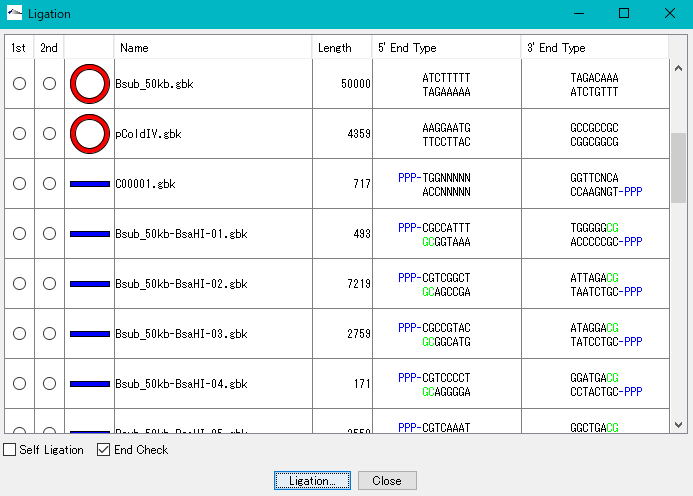
- ライゲーション産物として生成される塩基配列は、元の塩基配列と同様に解析することができます。
制限事項
- 現在、6個以上の塩基配列を連結するライゲーションはできません。
アルゴリズム
- IMC上で制限酵素切断された配列には、末端の状態を示す特殊なFeature KeyとQualifierが生成されます。
アミノ酸配列の解析機能です。アミノ酸プロファイル解析、Motif探索。
ゲノムアノテーションとは、ゲノムに注釈を加えることですが、より具体的には、ゲノム配列上に同定された特徴(Feature)の属性(Qualifier)を記述することです。
Featureの種類はFeature Key として分類されます。Featureの位置はPositionとして記録されます。ゲノム塩基配列上のPositionによって、そのFeatureが占める塩基配列が判ります。また、アミノ酸に翻訳されるコーディング領域(CDS)は、翻訳されたアミノ酸配列情報をGenetic Code Tableを介して間接的に保有することになります。CDSのようなフィーチャーは二重らせんのどちら側に特定されるかも重要で、通常はComplementという位置演算子を使って表記されています。
 |
- 多重ゲノム・アラインメント・フィーチャーマップ
- 染色体間での 相同性検索
- フィーチャーアラインメント、遺伝子クラスターアラインメント
- 環状ゲノムマップ (フィーチャーレイアウトスタイル 対応)
- ドットプロット
- 広域ゲノム再配置地図 作成(Global Genome Rearrangement Map)
- 局所ゲノム再配置地図 作成(Local Genome Rearrangement Map)
- ベン図 (Venn Diagram):オーソログ解析用
- コアゲノム解析
- 変異株間 変異抽出
- 反復配列検出
- 次世代シーケンサ からの 16SrRNA による メタゲノム解析
|
 |
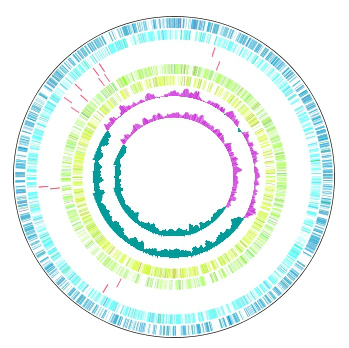
複数の近縁種ゲノムのフィーチャーや組成を同心円上に並列描画する機能です。
描画ダイアログから、同心円を自由に追加・編集・削除することができます。
- 複数の注釈付染色体塩基配列の任意のフィーチャーを表示
- 複数の染色体塩基配列の任意のコンテント・スキューを表示
- フィーチャー・コンテント表示順序変更
- GenomeMap表示指定フィーチャーのみの表示
- 同心円別の独立カラー設定
- レイアウトスタイルを登録し、多数のゲノムの環状ゲノムマップを効率よく作成
- 環状ゲノムマップの印刷(PDF,EMF,PNG)
- 実装:
 
|
- この機能は以下のエディションに実装されています。
- 2つのゲノム配列間の相同領域をドットマトリックスで表示します。
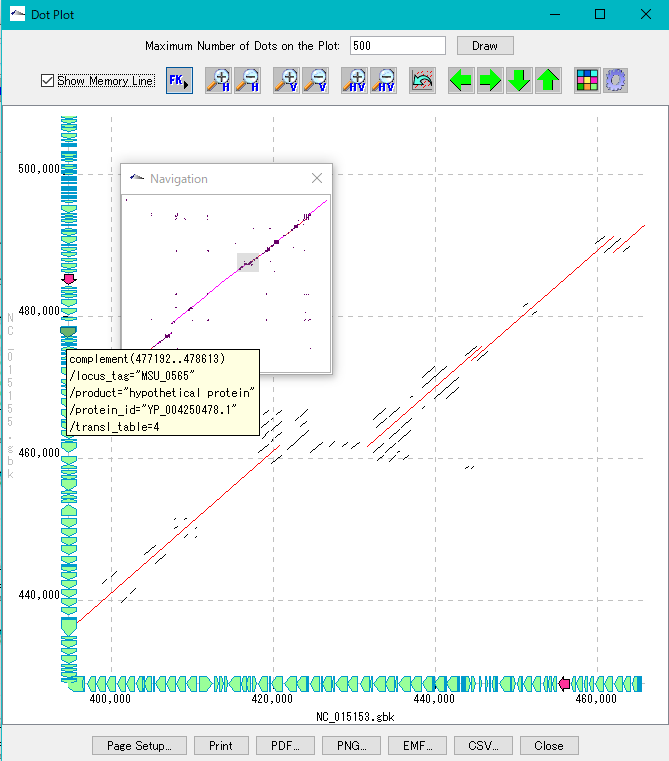
- カレントゲノム配列とカレント参照ディレクトリにロードされている1つのゲノム配列を選択して比較します。
- ドットカラーをOverlap塩基長、%Identigyの段階別に設定できます。結果表示画面では、ズーム、シフト、矩形で選択した任意の領域の拡大、ドットカラー設定、ナビゲーションウィンドウ、表示ドット数の制限、フィーチャーキー表示(フィーチャ―マウスオーバーで注釈を表示)が可能です。
- ドット画像は、PDF/PNG/EMF形式でファイル出力可能で、印刷設定も可能です。
- ドットリストはCSV形式でファイル出力可能です。
ベン図(Venn Diagram)は集合論で使用される図で、3個の集合(4集合以上の場合も描画可能ですが、IMCでは3集合以下のみ描画します)間の要素の数の分布を示したものです。
それぞれの集合に属する要素を円内に示し、それらが重なり会う部分を共通要素として示します。
生物学への応用として近縁種ゲノム間の相同遺伝子の数を図示することに使用されます。
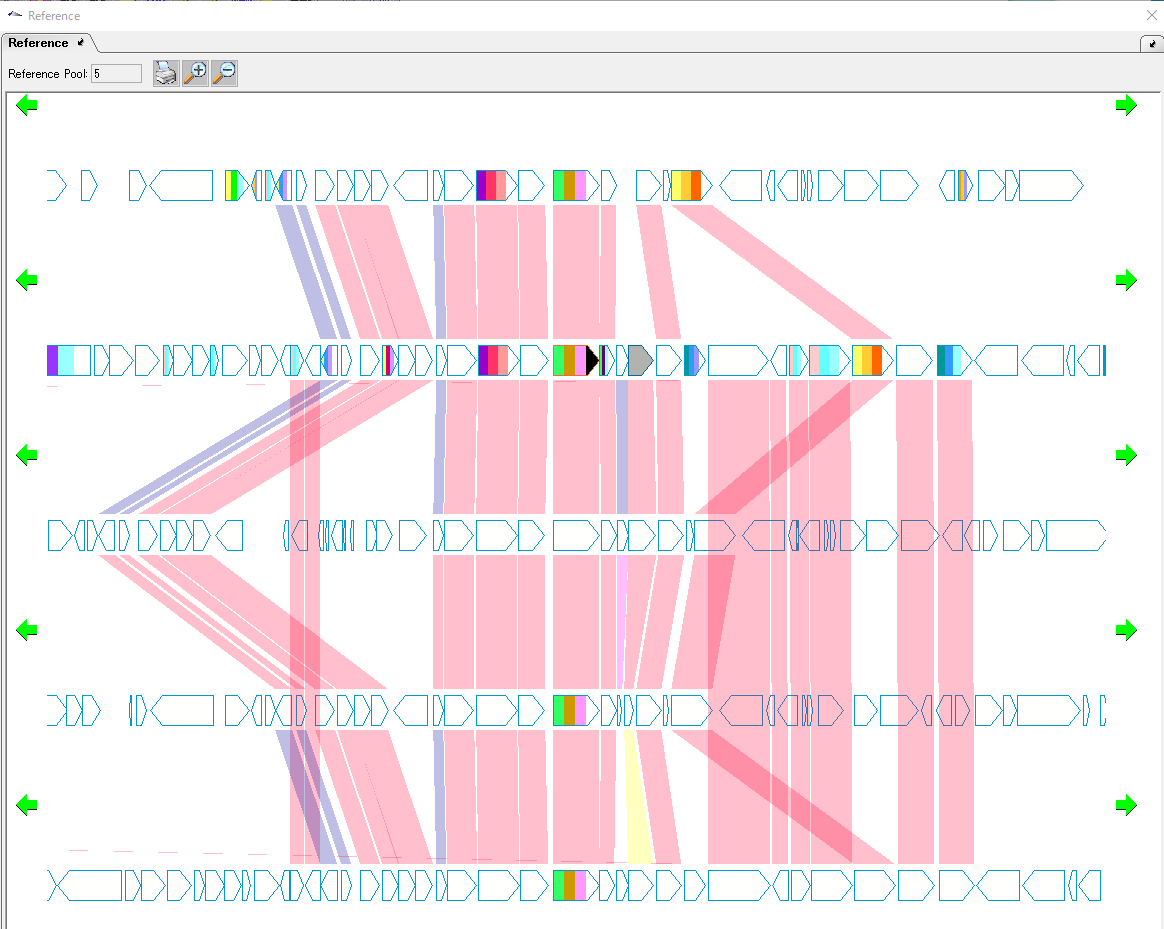
遺伝子クラスターアラインメントは、複数の近縁種ゲノムの1つの遺伝子に着目し、その近傍(上流にN個の遺伝子範囲、下流にN個の遺伝子範囲)を含めて、近縁種ゲノムとの間の相同性の有無を調べ、BBHがある場合には相同遺伝子同士を帯で結合表示するものです。
パンゲノムからコアゲノムを抽出します。
具体的には近縁種ゲノム集団から、共通遺伝子を抽出します。
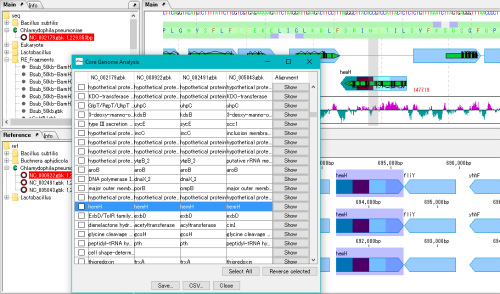
集団が大きい場合は計算時間がかかりますので、コア数の多い計算機で実行することを推奨します。
実装エディション:IMCGE ,AE
,AE ,DS
,DS
- 近縁種ゲノム(パンゲノム)間の変異点を塩基単位で検出します。
- カレントゲノム配列を基準として、カレント参照ディレクトリにロードされているゲノム配列から複数を選択し比較できます。
- ゲノム配列は遺伝子抽出されCDSフィーチャーが登録されている必要があります。
- 検出部位をCDS上あるいは遺伝子間領域のどちらかに設定できます。
- 検出判定基準については、%IdentityおよびOverlap率を変更できます。
- 解析結果画面には変異塩基のリストが表示され、表示項目はゲノム配列別に変異塩基、変異位置、gene name, ocus-Tagとなります。
- 結果はCSV形式でファイル出力できます。
- メモリーサイズを増やすと、解析可能なパンゲノムサイズも大きくなります。
| |
- 高精度なタイリングアレイデータを遺伝子などの注釈と併置して閲覧解析することが可能です。Affymetrix 社、Agilent 社、Nimblegen 社のアレイに対応しています。
- アレイプロファイル並列表示(レイアウトスタイル対応)
- アレイデータ補正、アレイ情報統計(グラフ作成)
- アレイ間演算、演算結果ファイル保存
- プローブレベルー遺伝子レベル発現強度変換
- 遺伝子(遺伝子間)別発現強度によるクラスタリング
- プロファイルピーク検出
|
異種宿主への組換用遺伝子組成設計について
コドン置換
組成自動設計
- 遺伝子クラスターをアライメントする機能
- Gibson Assembly, In-Fusionなどを利用した、遺伝子クラスター構築用プライマー自動デザイン機能
- Combinatorial Clusterを自動設計する
遺伝子クラスターが正しく設計されていかを検査する機能です。
- 宿主の組成にあった遺伝子組成、コドン組成を持っているか
- スタートコドン、ストップコドンは正しいか
- 必要な配列があるか
- 制限酵素認識部位
- RBS
- Homology Arm
- 不必要な配列がないか
- カレント配列を全フィーチャーを含めて、それまでの逆相補鎖を順鎖とする配置に変換し、フィーチャーマップも逆相補鎖を順鎖にして転回し、表示されます。
- 逆相補鎖変換された配列はその状態でファイル出力できます。
- ツールボタンは逆相補鎖ボタンのトグル表示となり、もう一度実行すると元の鎖に戻ります。
フィーチャーキーやフィーチャーなどのパラメータ設定を変更します。
NGSによる大規模シーケンシングと従来のキャピラリーシーケンサによるシーケンシングについての情報です。
NGSのデータ解析は、GenomeTravelerで実行できます。
キャピラリーシーケンシングデータ解析は、IMCで実行できます。
シーケンサからのリード配列を相同性を用いて互いに結合し、コンセンサス配列を生成します。
NGSからの大規模リードアセンブリとキャピラリーシーケンサからのアセンブリがあります。
NGSリードのアセンブリは、GenomeTravelerにおいて実行できます。
キャピラリーシーケンサからのリードアセンブリは、IMCのツールin silico Assemblerで実行可能です。
シーケンサからのリードの品質管理をします。
精度のよくない領域のトリミングや、全体的に精度の低いリードの排除を行い、アセンブリの精度を高めます。








 上下がオーバーラップするフィーチャーで、中央が演算生成されたフィーチャー。
上下がオーバーラップするフィーチャーで、中央が演算生成されたフィーチャー。